Lösungen
Contents
Lösungen#
Konfiguration und Python-Pakete#
import numpy as np
import matplotlib.pyplot as plt
# falls nicht vorhanden: conda install networkx pydot
import networkx as nx
from networkx.drawing.nx_pydot import graphviz_layout
import warnings
warnings.simplefilter(action='ignore', category=FutureWarning)
Aufgabe 1: Anwendungsbeispiele#
Nenen Sie mindestens fünf Anwendungsbeispiele von Graphen, die in der Vorlesung noch nicht genannt sind.
Lösung#
Inhaltsverzeichnis eines Buches -> Baum
elektrische Schaltungen
Kanalisation
das Gehirn
Zitatenetzwerk
Für mehr Beispiele siehe z. B. Wikipedia: Graph theory > Applications.
Aufgabe 2: Adjazenzmatrix#
Konstruieren und zeichnen Sie mit NetworkX einen Graphen \(G\) mit 5 Knoten und 5 Kanten, die einen Kreis bilden.
Mit dem Befehl
nx.adjacency_matrix(G).toarray()erhalten Sie die Adjazenzmatrix von \(G\). Was beschreibt Sie?Wie sieht ein Graph aus, dessen Adjazenzmatrix Nullen auf der Diagonalen hat und ansonsten Einträge 1 hat? Zeichnen Sie ein Beispiel auf.
Lösung#
G = nx.Graph()
G.add_edges_from([(1, 2), (2, 3), (3, 4), (4, 5), (5, 1)])
pos = nx.spring_layout(G)
nx.draw(G, pos=pos, with_labels=True, node_color='yellow')
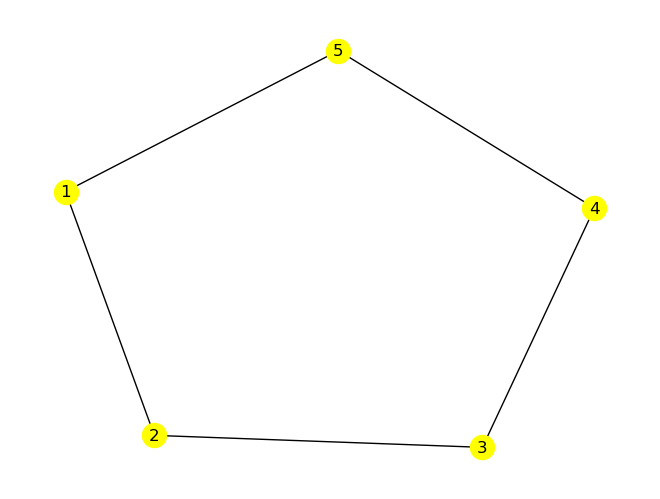
nx.adjacency_matrix(G).toarray()
array([[0, 1, 0, 0, 1],
[1, 0, 1, 0, 0],
[0, 1, 0, 1, 0],
[0, 0, 1, 0, 1],
[1, 0, 0, 1, 0]])
Siehe z. B. Wikipedia: Adjazenzmatrix.
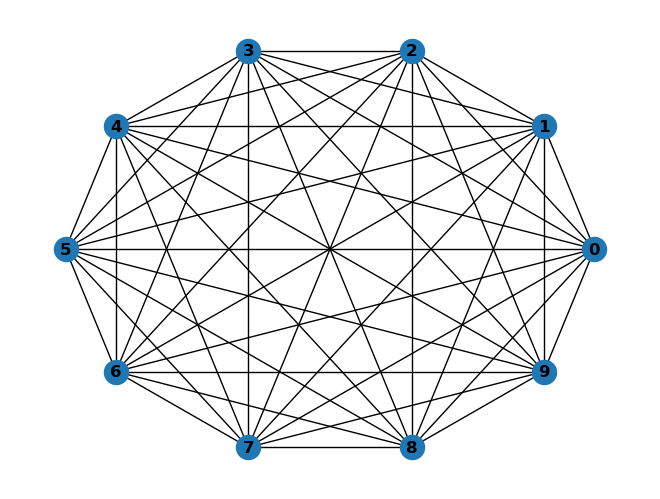
G = nx.complete_graph(10)
nx.draw_circular(G, with_labels=True, font_weight='bold')
nx.adjacency_matrix(G).toarray()
array([[0, 1, 1, 1, 1, 1, 1, 1, 1, 1],
[1, 0, 1, 1, 1, 1, 1, 1, 1, 1],
[1, 1, 0, 1, 1, 1, 1, 1, 1, 1],
[1, 1, 1, 0, 1, 1, 1, 1, 1, 1],
[1, 1, 1, 1, 0, 1, 1, 1, 1, 1],
[1, 1, 1, 1, 1, 0, 1, 1, 1, 1],
[1, 1, 1, 1, 1, 1, 0, 1, 1, 1],
[1, 1, 1, 1, 1, 1, 1, 0, 1, 1],
[1, 1, 1, 1, 1, 1, 1, 1, 0, 1],
[1, 1, 1, 1, 1, 1, 1, 1, 1, 0]])
Aufgabe 3: Breitensuche#
Implementieren Sie die Breitensuche mit einer Funktion, die den resultierenden Spannbaum als gerichteten Graphen zurückgibt. Vergleichen Sie Ihre Implementierung mit jener von NetworkX anhand mehrerer zufälliger, ungerichteter Graphen, die Sie z. B. mit dem Befehl gnm_random_graph erzeugen können.
Lösung#
G = nx.gnm_random_graph(n=10, m=15)
pos = nx.spring_layout(G, seed=0)
nx.draw(G, pos=pos, with_labels=True, node_color='yellow')
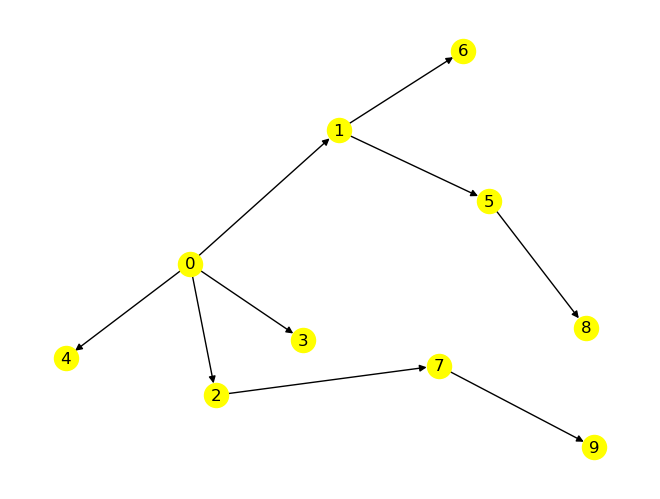
def my_plot(T, edges, node_start, pos):
nodes = [node_start] + [v for u, v in edges]
label = {}
counter = 0
for node in nodes:
label[node] = counter
counter += 1
nx.draw(T, pos, node_color='yellow')
nx.draw_networkx_labels(T, pos, label);
node_start = 0
T = nx.bfs_tree(G, node_start)
edges = nx.bfs_edges(G, node_start) # edges in bfs order
my_plot(T, edges, node_start, pos)
def my_add(node, nodes_visited, edges_traversed):
todo_new = []
for neighbor_node in G.neighbors(node):
if neighbor_node not in nodes_visited:
nodes_visited.append(neighbor_node)
edges_traversed.append((node, neighbor_node))
todo_new.append(neighbor_node)
return todo_new, nodes_visited, edges_traversed
def my_bfs(G, node_start):
nodes_visited = [node_start] # already visited
edges_traversed = [] # already traversed
todo = [node_start] # check neighbors of todo nodes
while len(todo):
doing = todo
todo = []
for node in doing:
print(f"current {node = }")
todo_new, nodes_visited, edges_traversed = my_add(node, nodes_visited, edges_traversed)
todo += todo_new
print(f" {todo_new = }")
print(f" {nodes_visited = }")
my_T = nx.DiGraph()
my_T.add_edges_from(edges_traversed)
return my_T, edges_traversed
my_T, my_edges = my_bfs(G, node_start)
my_plot(my_T, my_edges, node_start, pos)
current node = 0
todo_new = [1, 7, 8, 2]
nodes_visited = [0, 1, 7, 8, 2]
current node = 1
todo_new = [6, 9]
nodes_visited = [0, 1, 7, 8, 2, 6, 9]
current node = 7
todo_new = [4]
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4]
current node = 8
todo_new = []
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4]
current node = 2
todo_new = []
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4]
current node = 6
todo_new = [3]
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4, 3]
current node = 9
todo_new = []
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4, 3]
current node = 4
todo_new = [5]
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4, 3, 5]
current node = 3
todo_new = []
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4, 3, 5]
current node = 5
todo_new = []
nodes_visited = [0, 1, 7, 8, 2, 6, 9, 4, 3, 5]
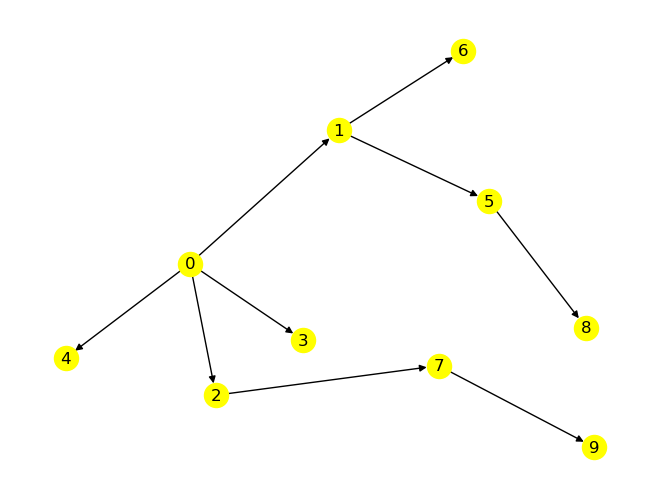
Aufgabe 4: Tiefensuche#
Implementieren Sie die Tiefensuche mit einer Funktion, die den resultierenden Spannbaum als gerichteten Graphen zurückgibt. Vergleichen Sie Ihre Implementierung mit jener von NetworkX anhand mehrerer zufälliger, ungerichteter Graphen, die Sie z. B. mit dem Befehl gnm_random_graph erzeugen können.
Hinweis: Mit G.nodes[node][attribute] = value können Sie dem Knoten node des Graphen G ein Attribute attribute mit Wert value zuweisen.
Lösung#
G = nx.gnm_random_graph(n=10, m=15)
pos = nx.spring_layout(G, seed=0)
nx.draw(G, pos=pos, with_labels=True, node_color='yellow')
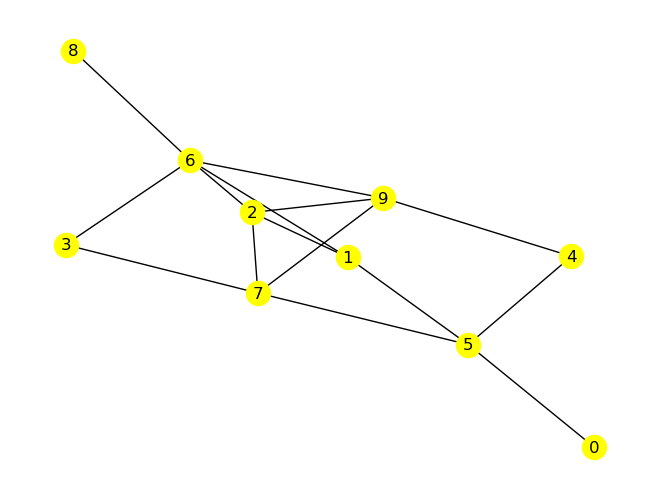
def my_plot(T, edges, node_start, pos):
nodes = [node_start] + [v for u, v in edges]
label = {}
counter = 0
for node in nodes:
label[node] = counter
counter += 1
nx.draw(T, pos, node_color='yellow')
nx.draw_networkx_labels(T, pos, label);
node_start = 0
T = nx.dfs_tree(G, node_start)
edges = nx.dfs_edges(G, node_start) # edges in dfs order
my_plot(T, edges, node_start, pos)
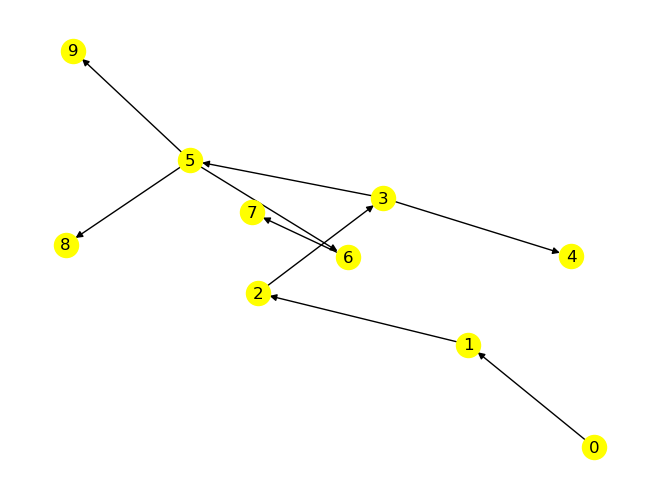
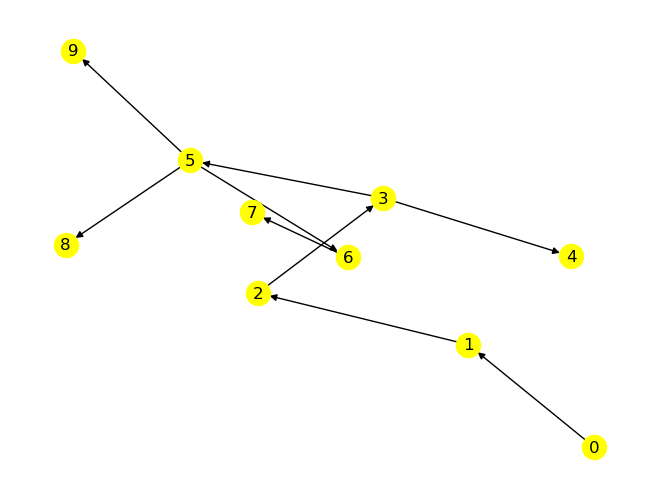
for node in G.nodes:
G.nodes[node]['visited'] = False
# G.nodes.data()
def my_traverse_from(node):
G.nodes[node]['visited'] = True
for neighbor_node in G.neighbors(node):
if not G.nodes[neighbor_node]['visited']:
edges_traversed.append((node, neighbor_node))
my_traverse_from(neighbor_node)
edges_traversed = []
my_traverse_from(node_start)
my_T = nx.DiGraph()
my_T.add_edges_from(edges_traversed)
# G.nodes.data()
my_plot(my_T, edges_traversed, node_start, pos)
Aufgabe 5: Dijkstra-Algorithmus#
Durch den Code unten ist ein ungerichteter Graph \(G\) definiert.
Führen Sie von Hand den Dijkstra-Algorithmus aus, indem Sie die Tabelle unten analog zur Vorlesung füllen.
S
B
C
D
E
F
G
H
0
ue.
ue.
ue.
ue.
ue.
ue.
ue.
Dabei steht ue. für unendlich.
Überprüfen Sie Ihr Ergebnis am Computer mit entsprechenden NetworkX-Funktionen.
G = nx.Graph()
G.add_edge('S', 'B', weight= 3)
G.add_edge('S', 'C', weight= 10)
G.add_edge('B', 'D', weight= 3)
G.add_edge('D', 'E', weight= 6)
G.add_edge('D', 'F', weight= 3)
G.add_edge('E', 'C', weight= 5)
G.add_edge('B', 'F', weight= 2)
G.add_edge('C', 'F', weight= 2)
G.add_edge('E', 'G', weight= 4)
G.add_edge('G', 'H', weight= 7)
G.add_edge('F', 'G', weight= 1)
G.add_edge('D', 'H', weight= 3)
pos = nx.spring_layout(G, seed=5)
nx.draw(G, pos=pos, with_labels=True, node_color='yellow')
edge_labels = nx.get_edge_attributes(G,'weight')
nx.draw_networkx_edge_labels(G, pos, edge_labels);
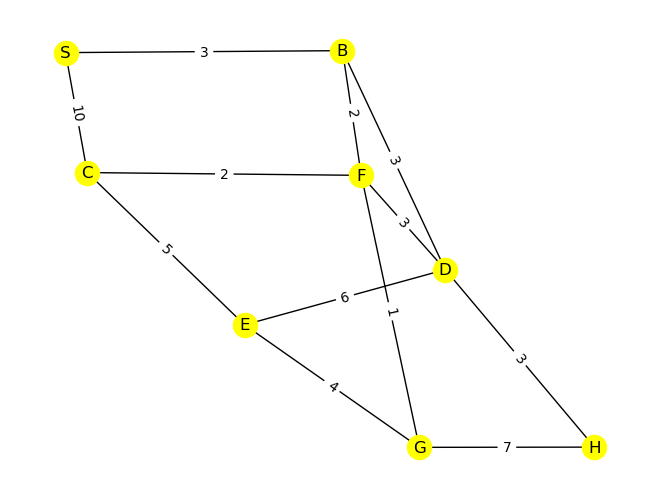
Lösung#
S |
B |
C |
D |
E |
F |
G |
H |
|---|---|---|---|---|---|---|---|
0 |
ue. |
ue. |
ue. |
ue. |
ue. |
ue. |
ue. |
- |
3\(_S\) |
10\(_S\) |
ue. |
ue. |
ue. |
ue. |
ue. |
- |
- |
10\(_S\) |
6\(_B\) |
ue. |
5\(_B\) |
ue. |
ue. |
- |
- |
7\(_F\) |
6\(_B\) |
ue. |
- |
6\(_F\) |
ue. |
- |
- |
7\(_F\) |
- |
12\(_D\) |
- |
6\(_F\) |
9\(_D\) |
- |
- |
7\(_F\) |
- |
10\(_G\) |
- |
- |
9\(_D\) |
- |
- |
- |
- |
10\(_G\) |
- |
- |
9\(_D\) |
- |
- |
- |
- |
10\(_G\) |
- |
- |
- |
nx.shortest_path(G, source='S', target=None, weight='weight')
{'S': ['S'],
'B': ['S', 'B'],
'C': ['S', 'B', 'F', 'C'],
'D': ['S', 'B', 'D'],
'F': ['S', 'B', 'F'],
'G': ['S', 'B', 'F', 'G'],
'E': ['S', 'B', 'F', 'G', 'E'],
'H': ['S', 'B', 'D', 'H']}
nx.shortest_path_length(G, source='S', target=None, weight='weight')
{'S': 0, 'B': 3, 'F': 5, 'D': 6, 'G': 6, 'C': 7, 'H': 9, 'E': 10}

